💻 Raster#
Ekstra biblioteker
Senere i denne notebooken skal vi bruke bibliotekene xarray og rioxarray, det kan være en god ide å installere de allerede nå, så det er klart til bruk senere:
conda install -c conda-forge xarray rioxarray
Rasterdata er mye brukt til å representere og lagre data om kontinuerlige overflater, der hver piksel inneholder spesifikk informasjon (karakteristikk, utstråling, spektralsignaturer) om et spesifikt område av jorden, for eksempel et 10x10 meter område. Denne notebooken gir en introduksjon til behandling av rasterdata i Python, og er basert på kapittel 7 i Python for Geographic Data Analysis
Det er forskjellige grunner til at du kanskje vil lagre dataene dine i rasterformat:
Det er en enkel datastruktur: En matrise av celler med verdier som representerer informasjon om den observerte overflaten/fenomenene
Det er en effektiv måte å lagre data fra store sammenhengende flater
Det er et kraftig format som kan brukes til ulike romlige og statistiske analyser
Du kan utføre raske overlay med flere lag
Arbeide med rasterdata i Python#
Det er en rekke biblioteker som er mye brukt når du arbeider med rasterdata i Python:
xarraygir en brukervennlig og intuitiv måte å jobbe med flerdimensjonale rasterdata med koordinater og attributter (noe likgeopandassom brukes til vektordatabehandling),rioxarraygir metoder for å utføre GIS-relaterte operasjoner med rasterdata (f.eks. lesing/skriving, reprojisering, klipping, resampling),“xarray-spatial” gir metoder for å analysere rasterdata (f.eks. fokale/sonale operasjoner, overflateanalyse, banefinning),
rasteriokjernebibliotek for arbeid med GIS-rasterdata.rioxarrayer en utvidelse av dette biblioteket som bringer de samme funksjonalitetene på toppen avxarray-biblioteket,numpyer et kjerne-bibliotek i Python for numerisk databehandling som brukes til å representere og arbeide med flerdimensjonale arrays.numpyhar stor innflytelse på hvordan de andre rasterbibliotekene fungerer og kan brukes til å generere flerdimensjonale arrays fra bunnen av.
Lage et enkelt rasterlag ved å bruke numpy#
For å få en bedre følelse av hvordan rasterdataene ser ut, kan vi starte med å lage en enkel todimensjonal array i Python ved å bruke numpy. I det følgende vil vi modifisere rasterlaget til å representere et enkelt terreng som har en høyde midt i rutenettet. Vi gjør dette ved å sette høyere verdier i midten mens de andre verdiene er representert med verdi 0. La oss starte med å importere numpy og matplotlib-biblioteket som vi bruker for å visualisere dataene våre:
import numpy as np
import matplotlib.pyplot as plt
Å lage et enkelt 2D-rasterlag (en 2D-matrise) med 10x10-matrise kan enkelt gjøres ved å bruke en numpy-metode .zeros() med fyller cellene (piksler) med nuller. Hver null representerer en standard pikselverdi (f.eks. 0 høyde). Du kan tenke på dette som et tomt rasternett:
raster_lag = np.zeros((10, 10))
raster_lag
array([[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[0., 0., 0., 0., 0., 0., 0., 0., 0., 0.]])
Nå har vi en enkel 2D-matrise fylt med nuller. Deretter modifiserer vi rasterlaget for å representere et enkelt terreng og legger til større tall i midten av rutenettet ved å sette høyere verdier i midten. Vi kan gjøre dette ved å slice numpy-matrisen ved å bruke indeksene til matrisen og oppdatere tallene på disse stedene til å være høyere. Å skjære “numpy”-matriser skjer på lignende måte som når du arbeider med Python-lister og får tilgang til elementene i en liste (se kapittel 2.2). Men i dette tilfellet gjør vi dette i to dimensjoner ved å få tilgang til verdiene som er lagret i spesifikke rader og kolonner ved å følge syntaksen: [start-rad-idx: end-row-idx, start-col-idx: end-col- idx]. Dermed kan vi oppdatere verdiene i vår 2D-matrise som følger:
raster_lag[4:7, 4:7] = 5
raster_lag[5, 5] = 10
raster_lag
array([[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[ 0., 0., 0., 0., 5., 5., 5., 0., 0., 0.],
[ 0., 0., 0., 0., 5., 10., 5., 0., 0., 0.],
[ 0., 0., 0., 0., 5., 5., 5., 0., 0., 0.],
[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.],
[ 0., 0., 0., 0., 0., 0., 0., 0., 0., 0.]])
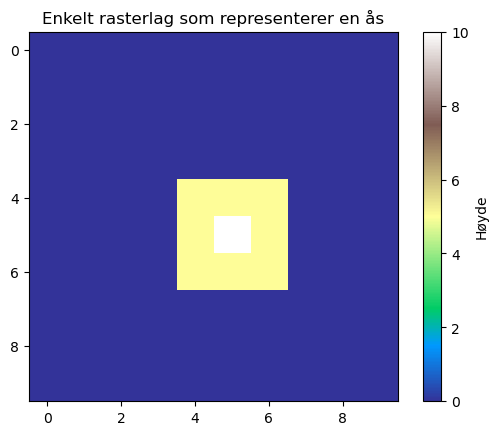
Her oppdaterte vi først cellene mellom den fjerde og syvende raden og kolonnen ([4:7, 4:7]) til å ha en verdi 5, og deretter oppdaterte vi midten av matrisen til å representere toppen av bakken med verdien 10. Som en Resultatet har vi et enkelt rasterlag som simulerer et enkelt terreng. Vi kan også plotte dette rasterlaget ved å bruke matplotlib-biblioteket og dets .imshow()-funksjon som kan brukes til å visualisere arrays:
plt.imshow(raster_lag, cmap='terrain')
plt.colorbar(label='Høyde')
plt.title('Enkelt rasterlag som representerer en ås')
plt.show()
Introduksjon til datastrukturer i xarray#
Nå som du har lært litt grunnleggende om rasterdata og hvordan du lager en enkel 2-dimensjonal raster-array ved å bruke “numpy”, fortsetter vi å utforske på en mer omfattende måte hvordan du arbeider med virkelige rasterdata ved å bruke “xarray” og rioxarray-biblioteker (+ andre relevante biblioteker knyttet til dem). xarray-biblioteket er et svært nyttig verktøy for å lagre, representere og manipulere rasterdata, mens rioxarray gir forskjellige rasterbehandlingsfunksjoner (GIS) på toppen av xarray-datastrukturene, for eksempel lesing og skriving av flere forskjellige rasterformater og utføre ulike geoberegningsoppgaver. Under panseret bruker rioxarray et annet Python-bibliotek kalt rasterio (som fungerer med N-dimensjonale numpy-matriser), men fordelen med xarray og rioxarray er at de gir en enklere og mer intuitiv måte å jobbe med rasterdatalag, på en litt lignende måte som å jobbe med vektordata ved å bruke geopandas.
Når du arbeider med rasterdata har du vanligvis ulike lag som representerer ulike geografiske trekk ved verden (f.eks. høyde, temperatur, nedbør osv.), og disse dataene blir muligens fanget opp på ulike tider av året/dagen/timen, noe som betyr at du har longitudinelle observasjoner fra samme område, som utgjør tidsseriedata. Oftere enn ikke må du kombinere informasjon fra disse lagene for å kunne gjennomføre meningsfulle analyser basert på dataene, for eksempel å lage en værmelding. En av de største fordelene med “xarray” er at du enkelt kan lagre, kombinere og analysere alle disse forskjellige lagene via et enkelt objekt, det vil si et “Dataset”, som vist i figur 7.2.
De to grunnleggende datastrukturene som tilbys av ‘xarray’-biblioteket er ‘DataArray’ og ‘Dataset’ (Figur 7.2). Begge bygger på og utvider styrkene til bibliotekene “numpy” og “pandas”. ‘DataArray’ er en merket N-dimensjonal array som ligner på ‘pandas.Series’ men fungerer med rasterdata (lagret som ‘numpy’ arrays). “Datasettet” er igjen en flerdimensjonal array-database i minnet som inneholder flere “DataArray”-objekter. I tillegg til variablene som inneholder observasjonene av et gitt fenomen, har du også x- og y-koordinatene til observasjonene lagret i separate lag, samt metadata som gir relevant informasjon om dataene dine, for eksempel Koordinatreferansesystem og /eller tid. Dermed er et “datasett” som inneholder rasterdata veldig likt “geopandas.GeoDataFrame”, og faktisk kan forskjellige “xarray”-operasjoner føles veldig kjent hvis du har lært det grunnleggende om “pandas” og “geopandas” dekket i kapittel 3 og 6.
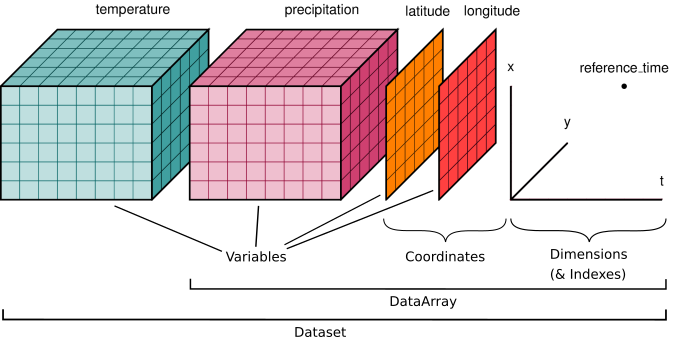
Figur 7.2 Nøkkel “xarray” datastrukturer. Bildekilde: Xarray Community (2024), lisensiert under Apache 2.0.
Noen av fordelene med “xarray” inkluderer:
Et mer intuitivt og brukervennlig grensesnitt for å jobbe med flerdimensjonale arrays (sammenlignet f.eks. med “numpy”)
Muligheten til å velge og kombinere data langs en dimensjon på tvers av alle arrays i et “Datasett” samtidig
Kompatibilitet med et stort økosystem av Python-biblioteker som fungerer med arrays/rasterdata
Tett integrering av funksjonaliteter fra velkjente Python-dataanalysebiblioteker, som “pandas”, “numpy”, “matplotlib” og “dask”.
Lese inn en fil#
Vi skal nå bruke xarray og rioaxarray til å lese inn rasterfilen vår. xarray og rioaxarray er ikke en del av oppsettet vi satte opp i conda-miljøet i starten av kurset. Hvis du ikke har installert det på egenhånd, kan det derfor være nødvendig å kjøre conda install -c conda-forge xarray rioxarray for å sørge for at den neste delen av notebooken fungerer.
import xarray as xr
import rasterio
from osgeo import gdal
import pathlib
NOTEBOOK_PATH = pathlib.Path().resolve()
DATA_MAPPE = NOTEBOOK_PATH / "data"
import rioxarray
url = DATA_MAPPE/"Aas_20240625.tif"
data = xr.open_dataset(url, engine='rasterio')
data
<xarray.Dataset> Size: 54MB
Dimensions: (band: 4, x: 2439, y: 1378)
Coordinates:
* band (band) int64 32B 1 2 3 4
* x (x) float64 20kB 5.911e+05 5.911e+05 ... 6.155e+05 6.155e+05
* y (y) float64 11kB 6.63e+06 6.63e+06 ... 6.616e+06 6.616e+06
spatial_ref int64 8B ...
Data variables:
band_data (band, y, x) float32 54MB ...Nå har vi lest GeoTIFF-filen inn i en xarray.Dataset datastruktur som vi lagret i en variabel data. “Datasettet” inneholder de faktiske dataverdiene for rastercellene, samt annen relevant attributtinformasjon relatert til dataene
type(data)
xarray.core.dataset.Dataset
# Koordinatene i datasettet
data.coords
Coordinates:
* band (band) int64 32B 1 2 3 4
* x (x) float64 20kB 5.911e+05 5.911e+05 ... 6.155e+05 6.155e+05
* y (y) float64 11kB 6.63e+06 6.63e+06 ... 6.616e+06 6.616e+06
spatial_ref int64 8B ...
# Projeksjonen til datasettet
data.rio.crs
CRS.from_epsg(32632)
# Variabler i datasettet
data.variables
Frozen({'band': <xarray.IndexVariable 'band' (band: 4)> Size: 32B
array([1, 2, 3, 4]), 'x': <xarray.IndexVariable 'x' (x: 2439)> Size: 20kB
array([591106.414369, 591116.413908, 591126.413447, ..., 615465.290753,
615475.290292, 615485.289831]), 'y': <xarray.IndexVariable 'y' (y: 1378)> Size: 11kB
array([6630014.779816, 6630004.777248, 6629994.774681, ..., 6616261.249119,
6616251.246552, 6616241.243984]), 'spatial_ref': <xarray.Variable ()> Size: 8B
[1 values with dtype=int64]
Attributes: (12/18)
crs_wkt: PROJCS["WGS 84 / UTM zone 32N",GEOGCS[...
semi_major_axis: 6378137.0
semi_minor_axis: 6356752.314245179
inverse_flattening: 298.257223563
reference_ellipsoid_name: WGS 84
longitude_of_prime_meridian: 0.0
... ...
longitude_of_central_meridian: 9.0
false_easting: 500000.0
false_northing: 0.0
scale_factor_at_central_meridian: 0.9996
spatial_ref: PROJCS["WGS 84 / UTM zone 32N",GEOGCS[...
GeoTransform: 591101.4146 9.999538745387454 0.0 6630..., 'band_data': <xarray.Variable (band: 4, y: 1378, x: 2439)> Size: 54MB
[13443768 values with dtype=float32]
Attributes:
AREA_OR_POINT: Area})
# Hvor mange og hvilke bånd
data.band.shape, data.band
((4,),
<xarray.DataArray 'band' (band: 4)> Size: 32B
array([1, 2, 3, 4])
Coordinates:
* band (band) int64 32B 1 2 3 4
spatial_ref int64 8B ...)
NDVI#
En vanlig operasjon er å beregne NDVI (Normalized difference vegetation index), noe som ganske enkelt lar seg gjøre:
NiR=data['band_data'][3,:,:]#Band 4 as counting starts from 0
Red=data['band_data'][2,:,:]#Band 3 as counting starts from 0
NDVI=(NiR-Red)/(NiR+Red)
NDVI
<xarray.DataArray 'band_data' (y: 1378, x: 2439)> Size: 13MB
array([[ 0.22876385, 0.22518766, 0.2872807 , ..., 0.19426751,
0.13308458, 0.10995542],
[ 0.20654206, 0.15864167, 0.21527778, ..., 0.22999737,
0.16201475, 0.09984276],
[ 0.22785808, 0.10348361, 0.1479719 , ..., 0.19976532,
0.07152034, 0.0209607 ],
...,
[-0.01456311, -0.02172164, -0.0016129 , ..., 0.542042 ,
0.44917086, 0.5226367 ],
[-0.01139138, -0.01818182, -0.001222 , ..., 0.5350183 ,
0.47758776, 0.4849965 ],
[-0.0070922 , -0.01260675, -0.01442308, ..., 0.5019272 ,
0.49319124, 0.44478807]], dtype=float32)
Coordinates:
* x (x) float64 20kB 5.911e+05 5.911e+05 ... 6.155e+05 6.155e+05
* y (y) float64 11kB 6.63e+06 6.63e+06 ... 6.616e+06 6.616e+06
spatial_ref int64 8B 0print('The variable type of the data:',type(NDVI))
print('The size of the data (first band):', NDVI.shape)
print('Minimum:', NDVI.min())
print('Maximum:', NDVI.max())
print('Mean:', NDVI.mean())
print('STD:', NDVI.std())
print('Data type of the array:',NDVI.dtype)
The variable type of the data: <class 'xarray.core.dataarray.DataArray'>
The size of the data (first band): (1378, 2439)
Minimum: <xarray.DataArray 'band_data' ()> Size: 4B
array(-0.43764818, dtype=float32)
Coordinates:
spatial_ref int64 8B 0
Maximum: <xarray.DataArray 'band_data' ()> Size: 4B
array(0.7736798, dtype=float32)
Coordinates:
spatial_ref int64 8B 0
Mean: <xarray.DataArray 'band_data' ()> Size: 4B
array(0.46235642, dtype=float32)
Coordinates:
spatial_ref int64 8B 0
STD: <xarray.DataArray 'band_data' ()> Size: 4B
array(0.15261656, dtype=float32)
Coordinates:
spatial_ref int64 8B 0
Data type of the array: float32
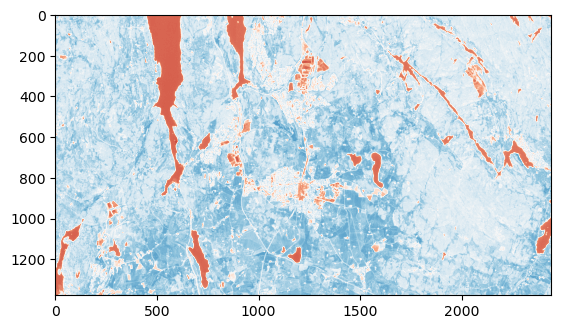
Vi kan også plotte NDVI-utregningen med plt.imshow()
plt.imshow(NDVI,vmin=-0.3, vmax=1,cmap='RdBu')
<matplotlib.image.AxesImage at 0x74a6cba46ea0>
Videre lesning#
Hvis du ønsker å lese mer om å jobbe med rasterdata i Python anbefaler jeg å ta en titt på:
